癫痫灶分析 SBM
病历一
一、Matlab→→spm→cat12→segment
- T1图像被归一化至模板空间,并分割为灰质(GM)、白质(WM)和脑脊液
- 预处理完成后,强烈建议进行质量检查.可通过“显示切片”和“检查样本”模块实现,这两个选项均位于CAT12窗口的“检查数据质量”栏目下。
- 在将GM图像输入统计模型前,需对图像数据进行平滑处理。需注意的是,该步骤未集成于CAT12工具箱,而是通过标准 SPM 模块“Smooth”实现。见Page12
segment→→Affine Regularisation ICBM space template – East Asian brains
二、CAT12 → Check data quality → Display slices
三、CAT12 → Statistical Analysis → Estimate TIV
XML files <-X → Select Files → [select xml-files] → Done
—Select the xml-files in the report-folder [e.g. the “cat_*.xml”].
Save values → TIV only
四、CAT12 → 检查数据质量 → 检查样本 → VBM 数据同质性
CAT12 → Check data quality → Check sample → VBM data homogeneity
五、CAT12 → 表面工具 → 表面重采样
CAT12 → Surface Tools → Resample Surfaces
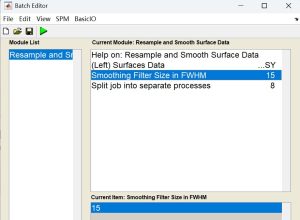
FWHM 中的平滑滤波器大小[使用默认值或修改]
– –12-15毫米的核素粒径被广泛用于SBM分析,建议厚度数据初始值采用15毫米,折叠数据(如脑回形成、复杂度)初始值采用20毫米
六、Building the Statistical Model
two-sample t-test
我们要找的是:患者组 < 对照组 的区域(灰质萎缩区)。
七、模型估计 (Model Estimation)
- 操作:CAT12 ->
Estimate,选择上一步生成的SPM.mat文件。 
CAT12—View models
- 对比设置 (Contrasts):
- 要寻找癫痫灶(萎缩区),设置 Contrast 为
[<span style="color: rgb(224, 62, 45);">1 -1]</span>(假设 Group 1 是患者,Group 2 是对照),即 Patient < Control。
- 要寻找癫痫灶(萎缩区),设置 Contrast 为
- 阈值设定:
- P-value:通常设为
0.001(未校正) 或0.05(FWE 校正,Family Wise Error)。 - Extent Threshold (k):设为
50或100个体素,去除噪点。
- P-value:通常设为
🧠 为什么要填 -1 1?
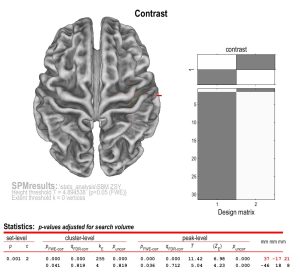
看右边的 Design Matrix(设计矩阵) 图:
- 左边灰色块:代表 Group 1 (你设置的 Patient 患者组)。
- 右边白色块:代表 Group 2 (你设置的 Control 对照组)。
你的目标是找 患者 < 对照 (即患者萎缩,体积更小) 的区域。
数学公式是:Control - Patient > 0
对应权重就是:(-1) * Patient + (1) * Control
所以权重向量是 [-1 1]。
| 如果你想找… | 权重向量 | 含义 |
|---|---|---|
| 患者萎缩区 (Patient < Control) | -1 1 |
✅ 这是你要选的! (癫痫灶通常是萎缩) |
| 患者增生区 (Patient > Control) | 1 -1 |
寻找灰质增多/肿胀 (较少见) |
| 任何差异 (双向) | 需定义两个对比 | 同时找萎缩和增生 |
填好并提交后,点击 OK。
SPM 会跳转到 Threshold 设置界面,那时记得按我们之前讨论的:
- P-value adjustment:
none - P-value:
0.001 - Extent threshold:
50 - 点击
Apply看结果!
![]()
